Je réaliserai toutes analyses en bioinformatique et apprentissage automatique
Bioinformatique, NGS, séq. scRNA, multi-omique, apprentissage automatique
À propos de ce service
Bonjour, je suis Sheraz, chercheur en bioinformatique et biologiste computationnel. Je me spécialise dans analyses avancées en bioinformatique et apprentissage automatique pour chercheurs, étudiants et organisations. J’aide à transformer des ensembles de données biologiques complexes en insights clairs et exploitables.
Avec cette service, je propose des solutions personnalisées pour une large gamme de données biologiques, y compris NGS (WGS, WES), RNA-seq, scRNA-seq, analyse CNV, génomique du cancer et datasets multi-omiques. J’implémente également modèles d’apprentissage automatique et d’IA pour l’analyse prédictive et la classification.
Mes services incluent :
- Prétraitement et QC des données : Nettoyage, normalisation et alignement
- Analyse statistique : Expression différentielle, sélection de caractéristiques et modélisation
- Apprentissage automatique et IA : Modélisation prédictive, clustering, classification et deep learning
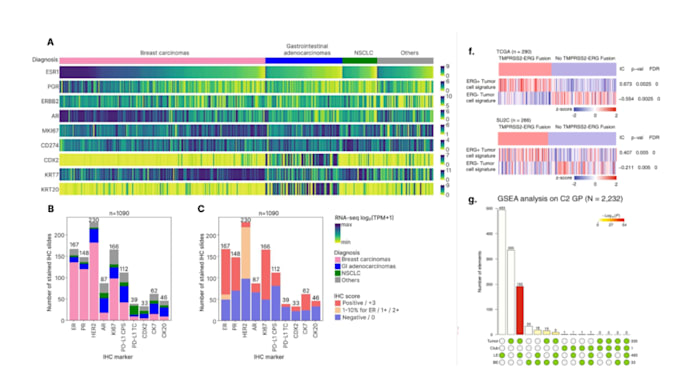
- Visualisation : PCA, heatmaps, volcano plots, diagrammes de réseau/voie
- Rapports détaillés : Résultats clairs, prêts pour publication avec interprétation biologique
Que vous ayez besoin d’un analyse bioinformatique de base ou d’un pipeline avancé d’apprentissage automatique, je fournis des résultats précis, reproductibles et de niveau recherche adaptés à votre projet.
Transformons vos données brutes en découvertes significatives !
Mon portfolio
FAQ
Traduction automatique
Quels types de données bioinformatiques analysez-vous ?
J’analyse des datasets NGS (WGS, WES, RNA-seq, scRNA-seq), données CNV, génomique du cancer et autres datasets multi-omiques. Je travaille également avec des datasets biologiques personnalisés pour l’analyse en apprentissage automatique.
Proposez-vous une analyse basée sur l’apprentissage automatique ou l’IA pour des données biologiques ?
Oui ! J’implémente des modèles d’apprentissage automatique, pipelines de deep learning, clustering, classification et analyse prédictive sur des datasets en bioinformatique et génomique.
Pouvez-vous traiter des données de séquençage brutes ?
Absolument. Je réalise le prétraitement des données brutes, le contrôle qualité, le trimming, l’alignement et la normalisation pour garantir des résultats propres et prêts pour publication.
Fournirez-vous des visualisations et des rapports ?
Oui, je fournis des visualisations de qualité publication telles que PCA, heatmaps, volcano plots et diagrammes de réseau/voie, accompagnées d’un rapport détaillé avec interprétation biologique.
Proposez-vous des conseils ou une orientation pour mon projet ?
Oui, je propose une consultation experte en bioinformatique et apprentissage automatique, pour vous guider dans la gestion des données, les stratégies d’analyse et l’interprétation efficace des résultats.
Pouvez-vous travailler sur des projets scRNA-seq ou multi-omiques ?
Absolument. Je suis spécialisé dans le scRNA-seq, l’intégration multi-omiques et l’analyse avancée en génomique avec des modèles d’apprentissage automatique.
Quels logiciels et outils utilisez-vous pour l’analyse ?
J’utilise Python, R, Linux, Bash, DESeq2, EdgeR, scikit-learn, TensorFlow, PyTorch, et d’autres outils en bioinformatique et ML pour fournir des résultats fiables et reproductibles.