Je vais effectuer un docking moléculaire et un criblage virtuel


À propos de ce service
Traduction automatique
Chercheur en MPhil spécialisé dans le docking moléculaire de haute précision et le criblage virtuel.
Vous avez besoin d’une modélisation computationnelle prête à publier pour votre thèse ou votre recherche ? Je propose des services d’in silico pour la découverte de médicaments en utilisant des protocoles standards de l’industrie afin d’assurer la précision géométrique et la stabilité de la liaison.
Services que je propose :
- Docking moléculaire : docking protéine-ligand avec AutoDock Vina, PyRx et CB-Dock2.
- Criblage virtuel : criblage à haut débit de bibliothèques chimiques pour identifier des composés principaux.
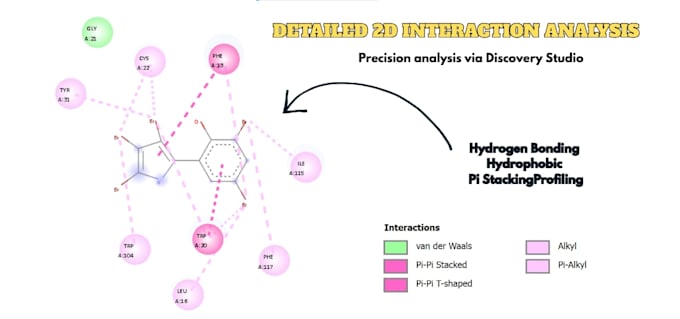
- Visualisation 3D : rendus haute résolution et cartographie des interactions avec PyMOL/Discovery Studio.
- Analyse post-docking : évaluation complète des affinités de liaison (kcal/mol) et de la stabilité des liaisons H-bond.
- Rapports techniques : analyses détaillées prêtes pour la soumission à une revue ou la soutenance académique.
Pourquoi choisir mes services ?
- Rigueur académique : résultats formatés selon les normes des revues W-Category.
- Expertise en logiciels : maîtrise de PyMOL, GROMACS et des suites AutoDock.
- Validation : protocoles incluant le Redocking pour garantir un RMSD inférieur à 2,0 Å.
Veuillez m’envoyer un message avec les détails de votre protéine (ID PDB) et de votre ligand avant de commander pour discuter de vos objectifs spécifiques !
Découvrez Anabia M.
MPhil Scholar, Bioinformatics and Drug Discovery Expert
- DePakistan
- Membre depuisoct. 2025
- Temps de réponse moy.1 heure
Langues
Anglais, Ourdou
Traduction automatique
Mon portfolio
FAQ
Traduction automatique
Quels fichiers dois-je fournir ?
Veuillez fournir : Protéine cible (ID PDB ou fichier). Ligands (format SDF ou MOL2). Informations sur la grille : si vous avez des coordonnées spécifiques (X, Y, Z) et des dimensions, veuillez les fournir. Sinon, indiquez si je dois effectuer un docking à l’aveugle ou si vous souhaitez spécifier les résidus du site actif.
Quel logiciel utilisez-vous pour le docking ?
J’utilise principalement AutoDock Vina et CB-Dock2, mais je peux m’adapter à d’autres outils spécifiques si nécessaire pour votre projet.
Pouvez-vous fournir des figures de qualité publication ?
Oui ! J’utilise Discovery Studio pour créer des graphiques d’interaction 3D et 2D haute résolution, prêts pour publication.
Proposez-vous des simulations de dynamique moléculaire (MD) ?
Mes forfaits standards se concentrent sur le docking, mais je peux réaliser des simulations MD en offre personnalisée. Veuillez me contacter pour discuter de la durée de la trajectoire.