Je réaliserai une analyse scRNA-seq et annotation des types de cellules
Développeur de pipelines bioinformatiques
À propos de ce service
Avez-vous des données de scRNA-seq qui nécessitent
une analyse professionnelle et une identification des types de cellules ?
J'analyserai votre jeu de données scRNA-seq en utilisant Seurat
et fournirai une annotation complète des types de cellules avec
des visualisations prêtes pour publication.
CE QUE VOUS OBTENEZ :
- Contrôle de qualité et filtrage des cellules de faible qualité
- Normalisation et mise à l’échelle
- Réduction de dimension PCA
- Clustering basé sur un graphe
- Visualisation UMAP
- Identification des gènes marqueurs par cluster
- Annotation biologique des types de cellules
- Rapport d’analyse complet
MON EXPÉRIENCE :
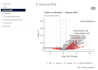
J'ai analysé 2 700 PBMC humains en identifiant 9 populations cellulaires distinctes
incluant les cellules T, B, NK, monocytes, cellules dendritiques et plaquettes en utilisant Seurat.
Pipeline complet disponible sur GitHub.
CE QUE J'AI BESOIN DE VOUS :
- Fichiers de sortie 10X Genomics (barcodes, features, matrix)
OU matrice de comptage traitée
- Nom de l’organisme (humain, souris, etc.)
- Toute information biologique connue sur votre échantillon
OUTILS : R, Seurat, ggplot2, dplyr, UMAP,
PCA, Git, Linux
Contactez-moi avant de commander pour discuter
de votre dataset. Je confirmerai d’abord la faisabilité.
Expertise:
Classification
•
regroupement
•
Analyse prédictive
Langage de programmation:
Python
•
R
Frameworks:
Panda
APIs:
Autres
Outils:
Jupyter Notebook
•
Colab